CRISPR
CRISPR (clustered regularly interspaced short palindromic repeats)序列是一组DNA它能识别入侵的细胞并利用一种酶将核糖核酸入侵者的核苷酸。它们是一种基本的免疫系统设备,检测并分裂病毒原核的生物。
研究人员使用crispr进行基因改造。它们对遗传学家来说具有独特的价值,因为它们分为两个阶段:首先,找到并定位特定的DNA链,然后,通过删除或替换该DNA反转录.CRISPR序列的这两个阶段比以前的方法更有效和准确。现在,研究人员可以同时使多个基因发生突变,这一过程在以前需要几个月或几年的时间,这对于研究由多个基因缺陷引起的单一疾病是必要的。研究人员已经使用crispr修饰农业植物,使它们更有营养、更抗瘟疫、更耐旱。在小鼠中,crispr已被用于纠正基因错误,包括导致镰状细胞贫血,肌肉萎缩症,以及与囊性纤维化.
crispr于2012年首次用于修饰人类细胞,推动了遗传学领域的快速技术变革,并引发了有关改造人类基因的伦理问题。
部分CRISPR序列
微生物宿主中的CRISPR序列由三部分组成:CRISPR相关(Cas)基因,即切割酶、tracrRNA和CRISPR RNA (crRNA)。tracrRNA和crRNA一起被称为引导RNA (gRNA)。一些CRISPR复合物还包括一条可插入目标的修复DNA链。
针对
gRNA链在CRISPR复合物中处理靶向。gRNA大约有80个碱基对,并与目标基因组结合以指导切割酶。三种类型(I-III)的CRISPR机制已经被确定,但类型II是最常用的,在这里描述。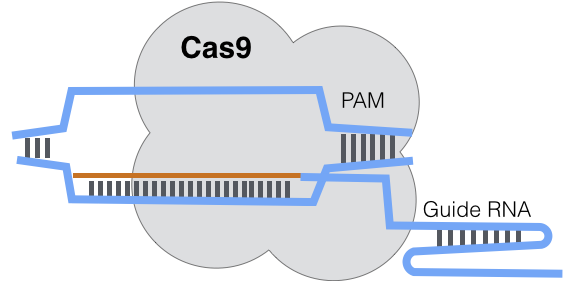 在微生物中,tracrRNA与入侵的DNA结合噬菌体而且质粒本质上是入侵病毒。在研究中,研究人员对tracrRNA进行定制,以找到并靶向他们想要编辑的任何基因,对tracrRNA的20个碱基对进行编码,以匹配他们想要在目标基因组中绑定的任何目标互补序列。
在微生物中,tracrRNA与入侵的DNA结合噬菌体而且质粒本质上是入侵病毒。在研究中,研究人员对tracrRNA进行定制,以找到并靶向他们想要编辑的任何基因,对tracrRNA的20个碱基对进行编码,以匹配他们想要在目标基因组中绑定的任何目标互补序列。
目标序列必须位于目标基因组中DNA的原间隔相邻基序(PAM)链的上游。目标基因组中的PAM本质上是一个标记和书夹,将细菌标记为目标,当gRNA读取PAM时停止结合。
一旦Cas-gRNA复合体(CRISPR序列)被表达,它就会改变了目标DNA和免疫印迹到它。这被称为双股断裂(DSB)。从本质上讲,Cas-gRNA复合体将两条DNA链分开,并与每条DNA链结合。如果tracrRNA和目标DNA足够相似,Cas酶就会切割目标DNA。
切酶
Cas是核酸酶,是crispr中的切割酶。在研究环境中最常用的Cas变体是Cas9。它来源于一种链球菌。Cas9通过两个核酸内切酶域的联合活性切割目标DNA,RuvC而且海航.
CRISPR系统的目标是以某种方式改变目标链,要么使其失去功能,要么以某种方式修复它。因此,一旦Cas酶切割了目标,它就会通过可选的修复DNA链插入新的DNA,删除现有的基因,或进行框架转移(将现有的碱基对移动到链上的其他位置)。
接下来,Cas重新连接分裂的DNA链使用非同源端连接(NHEJ)途径或同源定向修复(HDR)途径
兰德尔·普拉特成功地将Cas9酶植入小鼠胚胎,使其成为小鼠基因组的永久组成部分。Cas9小鼠已经成为CRISPR研究的重要工具,允许研究人员一次性针对多条DNA链并使它们全部突变。
一般来说,CRISPR研究是在小鼠身上进行的。自20世纪80年代以来,转基因小鼠一直是标准的试验对象。人类和老鼠在大约8000万年前拥有共同的祖先,今天老鼠的基因组被认为与人类的基因组非常相似,估计在70%到85%之间。老鼠还会患上复杂的疾病,影响它们的免疫系统和大脑。
有效性
CRISPR过程在多个阶段都有可能出现错误。首先,gRNA会偏离目标,与不相同的目标DNA链结合,修改错误的序列。在研究环境中,gRNA最好与目标DNA相同,并且在目标基因组中没有其他同源链。此外,当重新连接目标DNA时,非同源端连接(NHEJ)途径经常导致小的随机插入或删除。
CRISPR可以用来编辑和删除DNA的某些特定区域。CRISPR对哪类DNA区域的编辑/修饰最容易出错?
一个。着丝粒序列
B。小RNA簇区域
C。短串联重复序列
D。GAPDH开放阅读框
须考虑的问题:提出一些改进CRISPR过程以避免这些错误的方法。证明你的答案。
以前使用的,基因组编辑技术
在此之前,锌指(ZFs)和转录激活物样效应器(TALEs)是基因编辑的主要工具。但两者都需要为每个基因组目标构建定制的dna结合蛋白。它们既昂贵又耗时。然而,crispr使用标准的Cas切割酶(通常是Cas9)和从目标基因组拼接的短gRNA序列。从本质上讲,研究人员可以将他们想要靶向的突变基因连接到标准的切割工具上,然后设置它来删除或突变目标DNA。
